Todas las células de nuestro organismo contienen mutaciones somáticas, no obstante, sólo aquellas que adquieren un potencial maligno conducen al desarrollo del cáncer. Gracias a los avances en la secuenciación masiva, hoy en día se puede detectar toda clase de mutaciones presentes en el genoma tumoral (sustituciones, pequeñas inserciones y deleciones, reordenamientos cromosómicos y variación en el número de copias). Tradicionalmente, el enfoque ha estado en las mutaciones “driver”, que son aquellas que promueven el proceso neoplásico y confieren una ventaja evolutiva a la célula tumoral. Sin embargo, actualmente, existe un interés cada vez mayor por el análisis de la totalidad de mutaciones presentes en el tumor, incluyendo, además de las alteraciones “driver”, las mutaciones “passenger”, que son aquellas no implicadas en la tumorigénesis. Estas combinaciones únicas de mutaciones de las células reciben el nombre de firmas mutacionales (“mutational signatures”), y se producen como consecuencia de múltiples procesos mutacionales tales como errores en la replicación del ADN, agentes mutagénicos endógenos y exógenos, modificaciones enzimáticas del ADN o defectos en la maquinaria de reparación del ADN.
El grupo de investigación de Serena Nik Zainal, de la Universidad de Cambridge, en colaboración con el grupo de David H. Phillips, del King’s College London, ha publicado un estudio en Cell en el que exploran una serie de firmas mutacionales asociadas a agentes ambientales clasificados como conocidos, probables o posibles carcinógenos humanos.
A pesar de que la vinculación de la exposición a agentes ambientales con el cáncer se propuso por primera vez en el siglo XVIII, los mecanismos por los cuales estos agentes carcinógenos originan el cáncer aún no se comprenden en su totalidad.
Con el propósito de discernir el efecto mutagénico de los agentes medioambientales, los investigadores trataron células troncales pluripotentes inducidas humanas (IPS, por sus siglas en inglés) con 79 agentes ambientales pertenecientes a 13 familias, incluyendo radiación ultravioleta, el humo del tabaco, gases de escape y quimioterapéuticos, entre otros. Con el fin de que los resultados de los diferentes tratamientos fueran comparables entre sí, se empleó un diseño experimental altamente estandarizado. Además, dado que el cultivo celular puede ocasionar la adquisición de mutaciones, se incluyeron también clones control. Finalmente, a partir de las células tratadas y los controles, obtuvieron 324 subclones de célula única cuyo genoma fue secuenciado en su totalidad (WGS, por sus siglas en inglés) con el fin de detectar patrones de mutaciones.
Los análisis computacionales mostraron que todos los controles tenían unos patrones mutacionales similares, que definieron como mutagénesis “background”, ligada al cultivo celular. En aquellos agentes para los que se encontró firmas mutacionales asociadas, se eliminó la mutagénesis “background”, de manera que cada firma mutacional fuese resultado únicamente del daño en el ADN causado por el agente en cuestión.
El estudio reveló que el 52% de los agentes estudiados causaban firmas mutacionales patognomónicas. Concretamente, 41 agentes dieron lugar a firmas de sustitución, 6 agentes produjeron firmas de doble sustitución y 8 causaron firmas de pequeñas inserciones y deleciones (indels). Además, se observó que varias de las firmas mutacionales identificadas coincidían con firmas observadas en tumores humanos.
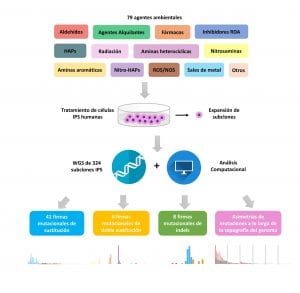
Imagen adaptada de Kucab JE, et al. A Compendium of Mutational Signatures of Environmental Agents. Cell. 2019.
Las dos firmas mutacionales de sustitución más destacadas fueron la resultante de la exposición a radiación solar simulada (transiciones C>T/G>A), que recapituló la firma observada en melanomas asociados a luz ultravioleta; y la ocasionada por ácidos aristolóquicos (transversiones A>T/T>A), simulando la firma de pacientes con tumores hepáticos o renales asociados al consumo de productos que contienen dichos ácidos.
Respecto a las firmas de dobles sustituciones, se observó que la exposición a radiación solar resultaba en un patrón distintivo de sustituciones CC>TT; que algunos de los hidrocarburos aromáticos policíclicos (HAPs) presentes en el humo del tabaco, concretamente el dibenzo[a,h] antraceno (DBA), el dibenzo[a,h] antraceno diol-epóxido (DBADE) y el benzo[a]pireno-7,8-dihidrodiol-9,10-epóxido (BPDE), generaban principalmente sustituciones GG>TT; y que los compuestos de platino (quimioterapéuticos) producían mayoritariamente sustituciones AG>TT.
En cuanto a indels, los investigadores observaron que la exposición a cisplatino producía una firma mutacional caracterizada por inserciones de T en sitios de una sola T o en un tramo de varias T localizados por debajo de dinucleótidos GpG que, curiosamente, constituyen las dianas de los entrecruzamientos entre cadenas que producen los compuestos de platino. Asimismo, entre los HAPs del humo del tabaco, el benzo[a]pireno (BaP), el BPDE y DBADE dieron lugar a patrones muy similares a las firmas de indels observadas en tumores de pulmón de pacientes fumadores.
Este estudio ha contribuido también a aumentar el conocimiento sobre los mecanismos de mutagénesis de los diferentes agentes carcinógenos. Respecto a los HAPs, se pudo observar la contribución de cada HAP en la firma COSMIC 4, observada en tumores de pulmón de fumadores, concretamente las sustituciones T>A/A>T ocasionadas por el dibenzo[a,l] pireno (DBP) y dibenzo[a,l] pireno diol-epóxido (DBPDE), y las dobles sustituciones e indels del BaP, BPDE, DBA y DBADE.
En cuanto a los radicales libres, la alteración más abundante fue la producción de 8-oxo-G, dando lugar a transversiones G>T/C>A. Además, las firmas ocasionadas por el bromato de potasio, la ocratoxina A y el metil eugenol resultaron similares a la firma COSMIC 18, anteriormente relacionada con las especies reactivas de oxígeno.
Cinco agentes alquilantes produjeron también firmas características. El N-etil-N-nitrosourea y N-metil-N-nitrosourea generaban firmas dominadas por transiciones T>C/A>G; las transiciones C>T/G>A predominaban en el caso del dietil sulfato y dimetil sulfato; y la 1,2-dimetilhidrazina producía ambos tipos de transiciones además de deleciones de C frecuentemente flanqueadas por T.
Por último, los compuestos de platino (cisplatino y carboplatino) produjeron firmas mutacionales de sustitución (transiciones G>A/C>T) y de dobles sustituciones (AG>TT y GA>TT), y el cisplatino dio lugar también a un patrón de inserciones de T. Es interesante señalar la similitud entre las firmas de estos compuestos y las firmas extraídas de pacientes con tumores mieloides que han recibido quimioterapia.
En el estudio se evaluó también la contribución de los diferentes mecanismos de reparación a las firmas mutacionales a partir del análisis de la asimetría de mutaciones a lo largo de la topografía del genoma. Estos análisis confirmaron que la respuesta al daño en el ADN, reparación de roturas de doble cadena, reparación de “mismatches” y reparación por escisión de nucleótidos están completamente operativos en las células IPS. Por ello, una alteración inicial puede dar lugar a diferentes firmas dependiendo del mecanismo de reparación que actúe.
En resumen, este estudio constituye una exploración de las firmas mutacionales causadas por mutágenos ambientales excluyendo el ruido presente en tumores humanos (debido a mutaciones ocasionadas por agentes endógenos y/o la variabilidad en la exposición a los agentes exógenos) y, por tanto, estos investigadores han generado un catálogo de firmas mutacionales ocasionadas exclusivamente por el daño en el ADN causado por agentes carcinógenos. Asimismo, este trabajo ha ampliado el conocimiento sobre los mecanismos de mutagénesis de los diferentes agentes ambientales y los distintos mecanismos de reparación del ADN que contribuyen a la firma mutacional final.
En el futuro, a medida que aumente la implementación de la secuenciación del genoma completo en cáncer, se podrá utilizar este catálogo de firmas mutacionales asociadas a agentes carcinógenos para discernir si la aparición del tumor se debe a una exposición ambiental. “Gracias a las firmas mutacionales, se puede tratar a los tumores como escenas de crimen, como si fuésemos científicos forenses, permitiéndonos identificar al culpable y los cómplices responsables de la aparición del tumor”, dijo la Dra. Serena Nik Zainal. Esta información puede ayudar a las investigaciones epidemiológicas en el descubrimiento de nuevas causas del cáncer, siendo de suma relevancia en salud pública, así como en la industria, para regular las exposiciones ocupacionales.
Referencia: Kucab JE, et al. A Compendium of Mutational Signatures of Environmental Agents. Cell. 2019 May 2;177(4):821-836.e16. doi: 10.1016/j.cell.2019.03.001.
Fuentes:
‘Fingerprint database’ could help to identify new cancer culprits. https://www.mrc-cu.cam.ac.uk/news/fingerprintdatabase
Causes of cancer may leave ‘fingerprints’ in DNA, scientists say. https://www.theguardian.com/science/2019/apr/15/causes-of-cancer-may-leave-fingerprints-in-dna-scientists-say
Si te ha gustado esta noticia y quieres aprender más sobre Genética en Cáncer, quizás te interesen nuestro curso de Medicina Genómica en Oncología y sus aplicaciones clínicas. Tienes más información aquí.

